公共卫生学院2011级预防医学七年制研究生范乾瑞作为第一作者的论文“GWAS summary-based pathway analysis correcting for the genetic confounding impact of environmental exposures”在国际生物信息学顶尖期刊《Briefings in Bioinformatics》上发表(2015年影响因子8.399,77个国际生物化学研究方法专业期刊排名第三)。国家卫计委“微量元素与地方病重点实验室”张峰是该论文的并列第一作者和通讯作者。
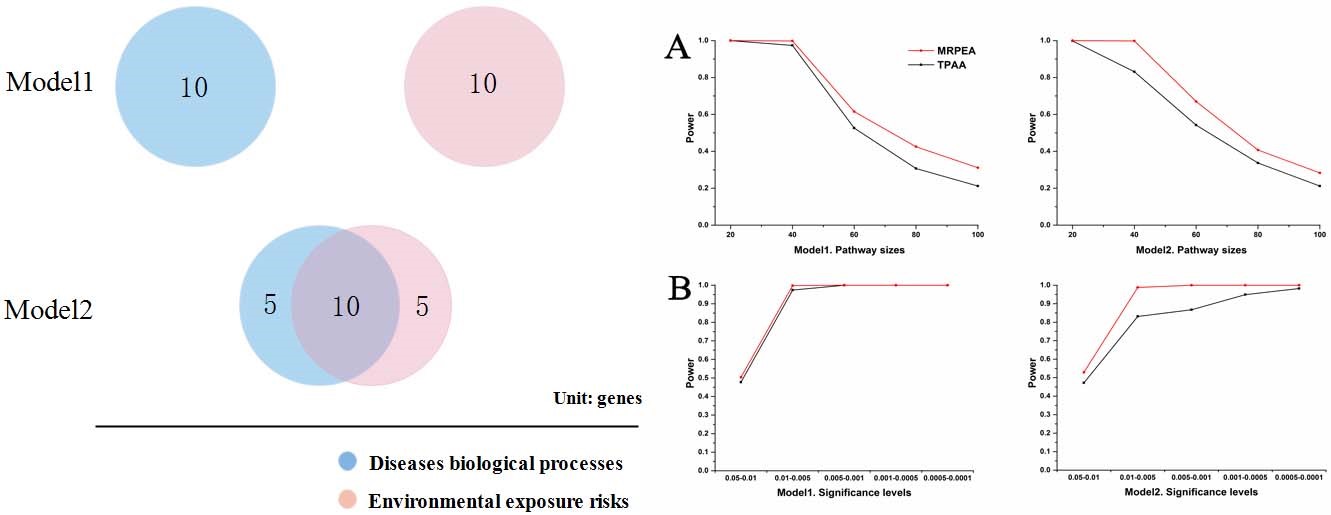
全基因组关联研究(Genome-wide association study,GWAS)是目前复杂疾病致病基因定位的主要方法之一,广泛应用于疾病的分子发病机制研究。然而,GWAS的统计效力易受环境混杂因素的干扰,导致假阳性结果,显著降低了GWAS的准确性。为了降低环境混杂因素对GWAS统计效力的影响,本研究采用孟德尔随机化(Mendelian randomization)分析和基因集富集分析算法,研发了可校正环境混杂因素的全基因组致病基因通路分析算法MRPEA。利用大规模的真实人群冠心病GWAS数据和基因组模拟分析发现MRPEA统计效力显著优于传统分析方法,显著提升了复杂疾病基因组数据分析的准确性。本研究还编写了相应的软件工具MRPEA(https://sourceforge.net/projects/mrpea/files),供研究者免费下载使用。
上述工作得到了国家自然科学基金的资助(81472925, 81673112)。2015年以来,张峰课题组在郭雄教授的指导下先后在Arthritis & Rheumatology、Briefings in Bioinformatics、Bioinformatics、Bone、Osteoarthritis Cartilage、Osteoporosis International等国际知名刊物上发表SCI论文17篇。第一作者论文先后被Science、PNAS、Neuron、Nature Review Neurology、Nature Review Genetics等国际权威期刊文章引用。
全文链接:
https://academic.oup.com/bib/article/doi/10.1093/bib/bbx025/3064182/GWAS-summary-based-pathway-analysis-correcting-for